



生物多样性 ›› 2026, Vol. 34 ›› Issue (1): 25364. DOI: 10.17520/biods.2025364 cstr: 32101.14.biods.2025364
谷际岐1, 赖江山2,3, 王瑛4, 吴浩然5, 张雪6, 宋晓彤7, 邵小明8,*( ), 娄安如1,*(
), 娄安如1,*( )
)
收稿日期:2025-09-09
接受日期:2026-01-08
出版日期:2026-01-20
发布日期:2026-02-06
通讯作者:
邵小明,娄安如
基金资助:
Jiqi Gu1, Jiangshan Lai2,3, Ying Wang4, Haoran Wu5, Xue Zhang6, Xiaotong Song7, Xiaoming Shao8,*( ), Anru Lou1,*(
), Anru Lou1,*( )
)
Received:2025-09-09
Accepted:2026-01-08
Online:2026-01-20
Published:2026-02-06
Contact:
Xiaoming Shao, Anru Lou
Supported by:摘要:
理解环境过滤、生物相互作用与中性过程如何共同塑造物种分布与群落结构, 是现代群落生态学的核心问题。然而, 传统多样性指数、排序分析及单物种分布模型(single-species distribution models, SDMs)难以同时整合物种间关联、环境梯度、性状与谱系等多维信息, 导致对群落构建机制的解析能力受限。联合物种分布模型(joint species distribution models, JSDMs)特别是生物群落层次建模(hierarchical modelling of species communities, HMSC)框架的提出, 为群落尺度的机制推断提供了统一而灵活的贝叶斯工具。本文系统综述了HMSC的统计结构、数学原理与推断机制, 构建了一个从数据组织、模型设定、马尔可夫链蒙特卡洛(Markov Chain Monte Carlo, MCMC)估计、模型评估到生态解释与预测的完整分析流程。同时结合苔藓群落数据配套编写了《联合物种分布模型HMSC的应用分步教程》, 通过分步讲解与可运行R代码, 助力研究者快速掌握该方法的实操应用。在理论部分, 本文明确了HMSC如何在统一的贝叶斯层级框架下整合环境梯度、物种性状、系统发育关系以及空间结构, 从而分离环境过滤、生物过滤与扩散限制的统计信号。在方法层面, 本文通过解析潜变量模型的数学结构, 阐明了残差相关在生态解释中的边界, 为理解物种共现信号、区分环境效应与未观测因子提供了理论依据; 对比了HMSC与其他主流JSDMs工具及传统群落统计方法的优势及适用性。在应用层面, 综述了其在森林、湿地、草原、海洋、城市及微生物生态学中的应用进展, 展示了其在保护规划、入侵种风险评估、共现网络分析及情景预测中的广泛价值; 随着图形处理器加速与迁移学习与大规模高维数据框架的发展, HMSC可提升稀有物种生态位估计与分布预测, 使数十万物种的群落建模成为可能。综上, JSDMs及HMSC不仅在生态统计方法论上实现了从单物种预测到多物种‒多维信息整合的跨越, 更为生态理论检验、群落构建机制解析及保护决策制定提供了高效、可扩展且能量化不确定性的工具平台。
谷际岐, 赖江山, 王瑛, 吴浩然, 张雪, 宋晓彤, 邵小明, 娄安如 (2026) 联合物种分布模型与生物群落层次建模框架: 生态学理论、方法及应用. 生物多样性, 34, 25364. DOI: 10.17520/biods.2025364.
Jiqi Gu, Jiangshan Lai, Ying Wang, Haoran Wu, Xue Zhang, Xiaotong Song, Xiaoming Shao, Anru Lou (2026) Theoretical foundations, methodological advances, and applications of joint species distribution models with a focus on the HMSC framework in ecology. Biodiversity Science, 34, 25364. DOI: 10.17520/biods.2025364.
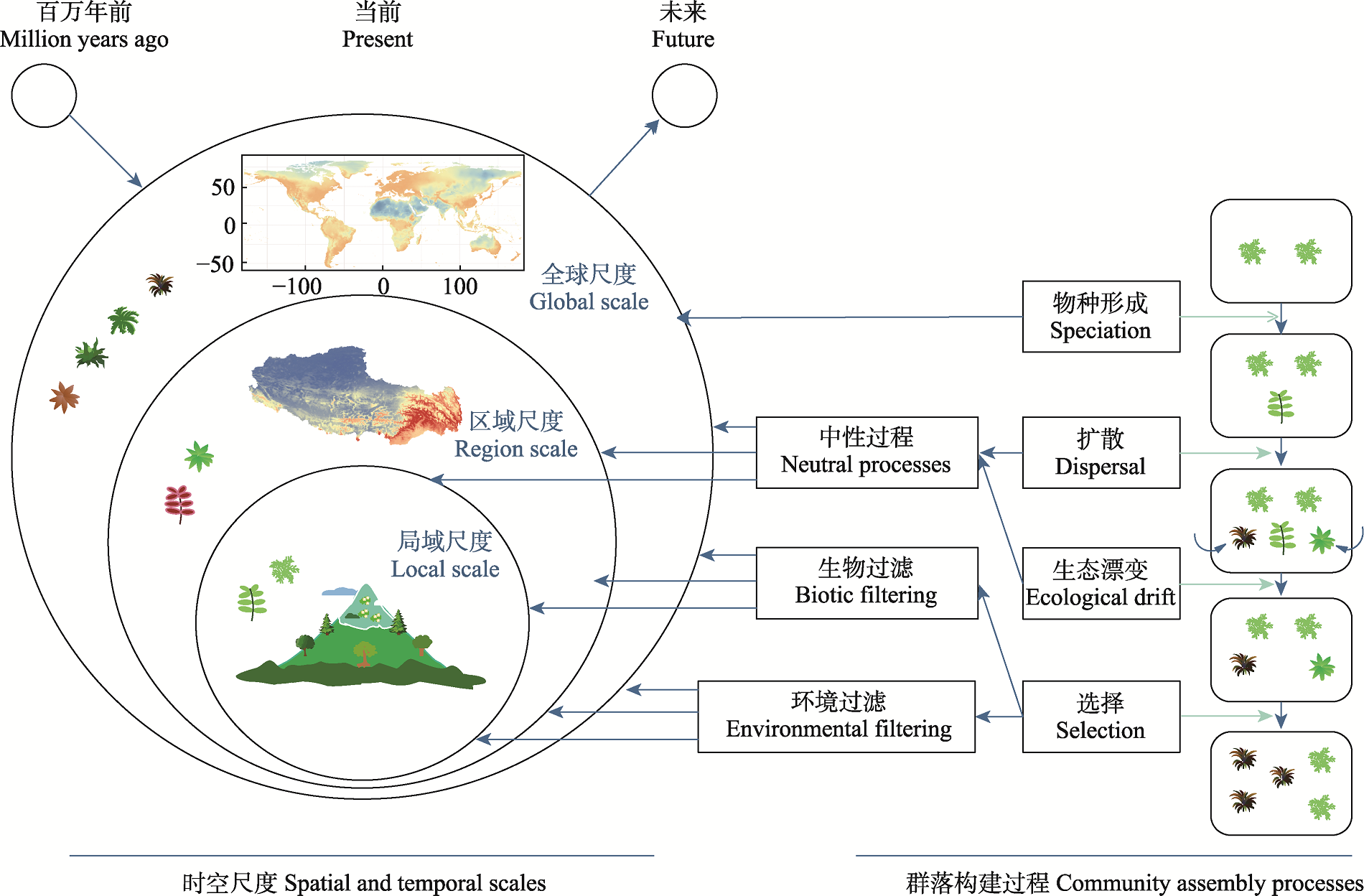
图1 群落构建过程的多尺度框架及观测数据类型示意图。图中展示了群落构建过程所处的不同时间与空间尺度, 包括全球尺度、区域尺度与局域尺度。群落构建过程可分为物种形成、中性过程(扩散、生态漂变等)、生物过滤(物种间相互作用)和环境过滤(非生物因子选择)等环节。蓝色箭头表示机制作用方向, 绿色箭头表示不同群落构建过程作用的路径。
Fig. 1 Schematic diagram of the multi-scale framework of community assembly processes and corresponding types of observational data. The figure illustrates the different temporal and spatial scales at which community assembly processes occur, including global, regional, and local scales. Community assembly processes can be divided into speciation, neutral processes (dispersal, ecological drift, etc.), biotic filtering (species interactions), and environmental filtering (selection by abiotic factors). Blue arrows indicate the direction of mechanisms, and green arrows denote the pathways of different community assembly processes.
| 索引及其范围 Index and range | 含义说明 Description |
|---|---|
| i = 1,..., n | 样方(采样单元) Sampling plots (Sampling units) |
| j = 1,..., ns | 物种 Species |
| k = 1,..., nc | 环境协变量 Environmental covariates |
| l = 1,..., nt | 物种性状 Species traits |
| h = 1,..., nf | 潜在因子 Latent factors |
| u = 1,..., nᵤ | 层级单元 Hierarchical units |
| q = 1,..., d | 空间坐标维度 Spatial coordinate dimensions |
| r = 1,..., nᵣ | 随机效应 Random effects |
表1 生物群落层次建模框架中的索引及其范围
Table 1 Indices and their ranges in the HMSC framwork
| 索引及其范围 Index and range | 含义说明 Description |
|---|---|
| i = 1,..., n | 样方(采样单元) Sampling plots (Sampling units) |
| j = 1,..., ns | 物种 Species |
| k = 1,..., nc | 环境协变量 Environmental covariates |
| l = 1,..., nt | 物种性状 Species traits |
| h = 1,..., nf | 潜在因子 Latent factors |
| u = 1,..., nᵤ | 层级单元 Hierarchical units |
| q = 1,..., d | 空间坐标维度 Spatial coordinate dimensions |
| r = 1,..., nᵣ | 随机效应 Random effects |
| 数据矩阵 Data matrix | 数据维度 Data dimension | 含义说明 Description |
|---|---|---|
| 𝐘, 元素 𝐘, elements | 群落数据 Community data | |
| 𝐗, 元素 𝐗, elements | 环境数据 Environmental data | |
| 𝐓, 元素 𝐓, elements | 物种性状数据 Species trait data | |
| 𝐂, 元素 𝐂, elements | 系统发育数据 Phylogenetic data | |
| 𝚷, 元素 𝚷, elements | 研究设计 Study design | |
| 𝐒, 元素 𝐒, elements | 空间坐标 Spatial coordinates |
表2 生物群落层次建模框架核心模型的数据矩阵及其维度
Table 2 Data matrices and their dimensions in the core model of HMSC framework
| 数据矩阵 Data matrix | 数据维度 Data dimension | 含义说明 Description |
|---|---|---|
| 𝐘, 元素 𝐘, elements | 群落数据 Community data | |
| 𝐗, 元素 𝐗, elements | 环境数据 Environmental data | |
| 𝐓, 元素 𝐓, elements | 物种性状数据 Species trait data | |
| 𝐂, 元素 𝐂, elements | 系统发育数据 Phylogenetic data | |
| 𝚷, 元素 𝚷, elements | 研究设计 Study design | |
| 𝐒, 元素 𝐒, elements | 空间坐标 Spatial coordinates |
| 类别 Category | 参数 Parameter | 类型 Type | 含义 Description |
|---|---|---|---|
| 固定效应 Fixed effect | LF, 元素 LF, elements | 固定效应的线性预测量 Linear predictor of fixed effects | |
| 固定效应 Fixed effect | B, 元素 B, elements | 物种生态位 Species ecological niches | |
| 固定效应 Fixed effect | M, 元素 M, elements | 基于性状的物种生态位期望值 Trait‐based expected values of species niches | |
| 固定效应 Fixed effect | ρ | 标量 Scalar | 物种生态位的系统发育信号 Phylogenetic signal in species niches |
| 固定效应 Fixed effect | Γ, 元素 Γ, elements | 性状对生态位的影响 Effects of traits on species niches | |
| 固定效应 Fixed effect | V, 元素 V, elements | 物种生态位的残差协方差 Residual covariance of species niches | |
| 随机效应 Random effect | Lᴿ, 元素 Lᴿ, elements | 随机效应的线性预测量 Linear predictor of random effects | |
| 随机效应 Random effect | H, 元素 H, elements | 样地载荷 Site loadings | |
| 随机效应 Random effect | α, 元素 α, elements | 长度为 Vector of length | 样地载荷的空间尺度 Spatial scale of site loadings |
| 随机效应 Random effect | Λ, 元素 Λ, elements | 物种载荷 Species loadings | |
| 随机效应 Random effect | Ω, 元素 Ω, elements | 物种间的关联关系 Interspecific association matrix | |
| 随机效应 Random effect | Φ, 元素 Φ, elements | 物种载荷的局部收缩项 Local shrinkage parameters of species loadings | |
| 随机效应 Random effect | δ, 元素 δ, elements | 长度为 vector of length | 物种载荷的全局收缩项 Global shrinkage parameters of species loadings |
| 数据模型 Data model | L, 元素 L, elements | 线性预测量 Linear predictor | |
| 数据模型 Data model | Σ, 元素 Σ, elements | 残差方差 Residual variances |
表3 生物群落层次建模(HMSC)框架核心模型中的参数及其解释
Table 3 Parameters in the core model of the HMSC framework and their interpretations
| 类别 Category | 参数 Parameter | 类型 Type | 含义 Description |
|---|---|---|---|
| 固定效应 Fixed effect | LF, 元素 LF, elements | 固定效应的线性预测量 Linear predictor of fixed effects | |
| 固定效应 Fixed effect | B, 元素 B, elements | 物种生态位 Species ecological niches | |
| 固定效应 Fixed effect | M, 元素 M, elements | 基于性状的物种生态位期望值 Trait‐based expected values of species niches | |
| 固定效应 Fixed effect | ρ | 标量 Scalar | 物种生态位的系统发育信号 Phylogenetic signal in species niches |
| 固定效应 Fixed effect | Γ, 元素 Γ, elements | 性状对生态位的影响 Effects of traits on species niches | |
| 固定效应 Fixed effect | V, 元素 V, elements | 物种生态位的残差协方差 Residual covariance of species niches | |
| 随机效应 Random effect | Lᴿ, 元素 Lᴿ, elements | 随机效应的线性预测量 Linear predictor of random effects | |
| 随机效应 Random effect | H, 元素 H, elements | 样地载荷 Site loadings | |
| 随机效应 Random effect | α, 元素 α, elements | 长度为 Vector of length | 样地载荷的空间尺度 Spatial scale of site loadings |
| 随机效应 Random effect | Λ, 元素 Λ, elements | 物种载荷 Species loadings | |
| 随机效应 Random effect | Ω, 元素 Ω, elements | 物种间的关联关系 Interspecific association matrix | |
| 随机效应 Random effect | Φ, 元素 Φ, elements | 物种载荷的局部收缩项 Local shrinkage parameters of species loadings | |
| 随机效应 Random effect | δ, 元素 δ, elements | 长度为 vector of length | 物种载荷的全局收缩项 Global shrinkage parameters of species loadings |
| 数据模型 Data model | L, 元素 L, elements | 线性预测量 Linear predictor | |
| 数据模型 Data model | Σ, 元素 Σ, elements | 残差方差 Residual variances |
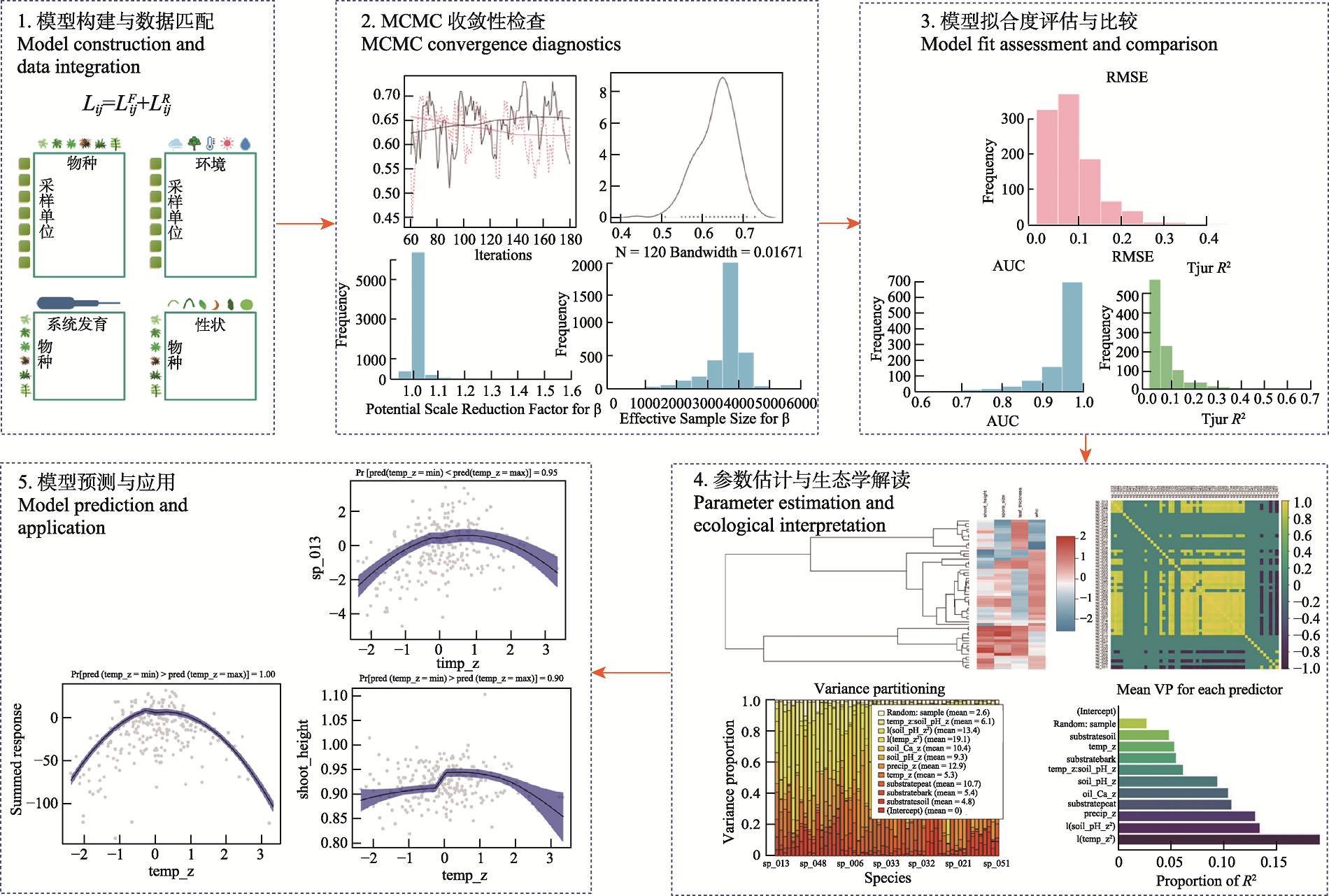
图2 生物群落层次建模(HMSC)框架的完整分析流程与结果示意。图中依次展示了HMSC建模与推断的5个关键步骤: (1)模型构建与数据匹配, 将物种分布数据与环境因子、功能性状、系统发育和空间随机效应整合到统一的层级贝叶斯框架中; (2) MCMC收敛性检查, 通过迹线图、后验分布、有效样本量和潜在尺度缩减因子评估模型收敛与参数混合情况; (3)模型拟合度评估与比较, 利用均方根误差(RMSE)、曲线下面积(AUC)和R2等指标量化模型预测性能; (4)参数估计与生态解释, 包括环境响应参数、性状与系统发育效应、残差相关结构以及方差分解结果; (5)模型预测与应用, 展示物种对关键环境梯度的响应曲线及不确定性区间, 用于群落分布预测与情景分析。
Fig. 2 Schematic overview of the complete analytical workflow and outputs of hierarchical modelling of species communities (HMSC) framework. The figure illustrates five key steps of HMSC-based modelling and inference: (1) model construction and data integration, in which species distribution data are jointly modelled with environmental variables, functional traits, phylogenetic relationships, and spatial random effects within a unified hierarchical Bayesian framework; (2) MCMC convergence diagnostics, where trace plots, posterior distributions, effective sample size (ESS), and potential scale reduction factors (PSRF) are used to assess convergence and fitness parameter mixing; (3) model fit evaluation and comparison, in which predictive performance is quantified using root mean square error (RMSE), area under curve (AUC), and R²; (4) parameter estimation and ecological interpretation, including environmental response parameters, trait and phylogenetic effects, residual correlation structures, and variance partitioning; and (5) model prediction and application, illustrating species responses to key environmental gradients with associated uncertainty intervals for community-level prediction and scenario-based analyses.
| [1] | Abrego N, Niittynen P, Kemppinen J, Ovaskainen O (2025) Joint species-trait distribution modeling: The role of intraspecific trait variation in community assembly. Ecology, 106, e70174. |
| [2] | Abrego N, Norberg A, Ovaskainen O (2017) Measuring and predicting the influence of traits on the assembly processes of wood-inhabiting fungi. Journal of Ecology, 105, 1070-1081. |
| [3] | Agrawal AA, Ackerly DD, Adler F, Arnold AE, Cáceres C, Doak DF, Post E, Hudson PJ, Maron J, Mooney KA, Power M, Schemske D, Stachowicz J, Strauss S, Turner MG, Werner E (2007) Filling key gaps in population and community ecology. Frontiers in Ecology and the Environment, 5, 145-152. |
| [4] | Anderson MJ, Walsh DCI (2013) PERMANOVA, ANOSIM, and the Mantel test in the face of heterogeneous dispersions: What null hypothesis are you testing? Ecological Monographs, 83, 557-574. |
| [5] | Begon M, Townsend CR (2020) Ecology: From Individuals to Ecosystems, 5th edn. John Wiley & Sons, Hoboken, USA. |
| [6] | Blanchet FG, Cazelles K, Gravel D (2020) Co-occurrence is not evidence of ecological interactions. Ecology Letters, 23, 1050-1063. |
| [7] | Bohmann K, Evans A, Gilbert MTP, Carvalho GR, Creer S, Knapp M, Yu DW, de Bruyn M (2014) Environmental DNA for wildlife biology and biodiversity monitoring. Trends in Ecology & Evolution, 29, 358-367. |
| [8] | Breiner FT, Guisan A, Bergamini A, Nobis MP (2015) Overcoming limitations of modelling rare species by using ensembles of small models. Methods in Ecology and Evolution, 6, 1210-1218. |
| [9] | Calabrese JM, Certain G, Kraan C, Dormann CF (2014) Stacking species distribution models and adjusting bias by linking them to macroecological models. Global Ecology and Biogeography, 23, 99-112. |
| [10] | Chase JM, Myers JA (2011) Disentangling the importance of ecological niches from stochastic processes across scales. Philosophical Transactions of the Royal Society of London Series B, Biological Sciences, 366, 2351-2363. |
| [11] | Clark JS, Nemergut D, Seyednasrollah B, Turner PJ, Zhang S (2017) Generalized joint attribute modeling for biodiversity analysis: Median-zero, multivariate, multifarious data. Ecological Monographs, 87, 34-56. |
| [12] | Cranston A, Cooper N, Bro-Jørgensen J (2024) Using joint species distribution modelling to identify climatic and non-climatic drivers of Afrotropical ungulate distributions. Ecography, 2024, e07209. |
| [13] | Dormann CF, Bobrowski M, Dehling DM, Harris DJ, Hartig F, Lischke H, Moretti MD, Pagel J, Pinkert S, Schleuning M, Schmidt SI, Storch I, Weiss IS, Mueller J (2018) Biotic interactions in species distribution modelling: 15 challenges and a way forward. Ecography, 41, 1-15. |
| [14] | Doser JW, Finley AO, Kéry M, Zipkin EF (2022) spOccupancy: An R package for single-species, multi-species, and integrated spatial occupancy models. Methods in Ecology and Evolution, 13, 1670-1678. |
| [15] | Dray S, Legendre P (2008) Testing the species traits-environment relationships: The fourth-corner problem revisited. Ecology, 89, 3400-3412. |
| [16] | Elith J, Leathwick JR (2009) Species distribution models: Ecological explanation and prediction across space and time. Annual Review of Ecology, Evolution, and Systematics, 40, 677-697. |
| [17] | Epele LB, Williams-Subiza EA, Bird MS, Boissezon A, Boix D, Demierre E, Fair CG, García PE, Gascón S, Grech MG, Greig HS, Jeffries M, Kneitel JM, Loskutova O, Maltchik L, Manzo LM, Mataloni G, McLean K, Mlambo MC, Oertli B, Pires MM, Sala J, Scheibler EE, Stenert C, Wu HT, Wissinger SA, Batzer DP (2024) A global assessment of environmental and climate influences on wetland macroinvertebrate community structure and function. Global Change Biology, 30, e17173. |
| [18] | Escamilla Molgora JM, Sedda L, Diggle PJ, Atkinson PM (2022) A taxonomic-based joint species distribution model for presence-only data. Journal of the Royal Society, Interface 19, 20210681. |
| [19] | Fang XN, Zhang P, Xing QW, Chen XJ, Cao J, Zhang H, Yu W (2025) The impact of varying spatiotemporal scales on different joint species distribution models: A case study of pelagic fish species in the northwest Pacific Ocean. Journal of Biogeography, 52, e15154. |
| [20] | Fick SE, Hijmans RJ (2017) WorldClim 2: New 1-km spatial resolution climate surfaces for global land areas. International Journal of Climatology, 37, 4302-4315. |
| [21] | Galante PJ, Alade B, Muscarella R, Jansa SA, Goodman SM, Anderson RP (2018) The challenge of modeling niches and distributions for data-poor species: A comprehensive approach to model complexity. Ecography, 41, 726-736. |
| [22] | Gilarranz LJ, Rayfield B, Liñán-Cembrano G, Bascompte J, Gonzalez A (2017) Effects of network modularity on the spread of perturbation impact in experimental metapopulations. Science, 357, 199-201. |
| [23] | Gotelli NJ (2000) Null model analysis of species co-occurrence patterns. Ecology, 81, 2606-2621. |
| [24] | Gotelli N, Hart E, Ellison A, Hart ME (2015) Package ‘EcoSimR’. R Package. Available at: https://CRAN.R-project.org/package=EcoSimR. (accessed on 2026-01-10) |
| [25] | Götzenberger L, de Bello F, Bråthen KA, Davison J, Dubuis A, Guisan A, Lepš J, Lindborg R, Moora M, Pärtel M, Pellissier L, Pottier J, Vittoz P, Zobel K, Zobel M (2012) Ecological assembly rules in plant communities— Approaches, patterns and prospects. Biological Reviews, 87, 111-127. |
| [26] | Guisan A, Thuiller W (2005) Predicting species distribution: Offering more than simple habitat models. Ecology Letters, 8, 993-1009. |
| [27] | Huang EH, Ji CJ, Liang MX, Zhu JL, Tang ZY, Fang JY (2025) Climatic and non-climatic effects on species occurrence and abundance shift in different trends along elevational gradients. Journal of Plant Ecology, 18, rtaf122. |
| [28] | Hui FKC (2016) Boral-Bayesian ordination and regression analysis of multivariate abundance data in R. Methods in Ecology and Evolution, 7, 744-750. |
| [29] | Hui FKC, Taskinen S, Pledger S, Foster SD, Warton DI (2015) Model-based approaches to unconstrained ordination. Methods in Ecology and Evolution, 6, 399-411. |
| [30] | Itter MS, Kaarlejärvi E, Laine AL, Hamberg L, Tonteri T, Vanhatalo J (2024) Bayesian joint species distribution model selection for community-level prediction. Global Ecology and Biogeography, 33, e13827. |
| [31] | Jeliazkov A, Gavish Y, Marsh CJ, Geschke J, Brummitt N, Rocchini D, Haase P, Kunin WE, Henle K (2022) Sampling and modelling rare species: Conceptual guidelines for the neglected majority. Global Change Biology, 28, 3754-3777. |
| [32] | Kattge J, Diaz S, Lavorel S, Prentice IC, Leadley P, Bönisch G, Garnier E, Westoby M, Reich PB, Wright IJ (2011) TRY—A global database of plant traits. Global Change Biology, 17, 2905-2935. |
| [33] | Korhonen P, Hui FKC, Niku J, Taskinen S, van der Veen B (2024) A comparison of joint species distribution models for percent cover data. Methods in Ecology and Evolution, 15, 2359-2372. |
| [34] | Kraft NJB, Adler PB, Godoy O, James EC, Fuller S, Levine JM (2015) Community assembly, coexistence and the environmental filtering metaphor. Functional Ecology, 29, 592-599. |
| [35] | Legendre P, Galzin R, Harmelin-Vivien ML (1997) Relating behavior to habitat: Solutions to the fourth-corner problem. Ecology, 78, 547-562. |
| [36] | Legendre P, Legendre L (2012) Numerical Ecology. Elsevier, Amsterdam. |
| [37] | Leibold MA, Holyoak M, Mouquet N, Amarasekare P, Chase JM, Hoopes MF, Holt RD, Shurin JB, Law R, Tilman D, Loreau M, Gonzalez A (2004) The metacommunity concept: A framework for multi-scale community ecology. Ecology Letters, 7, 601-613. |
| [38] | Liu C, Van Meerbeek K (2024) Predicting the responses of European grassland communities to climate and land cover change. Philosophical Transactions of the Royal Society of London Series B, Biological Sciences, 379, 20230335. |
| [39] | Logue JB, Mouquet N, Peter H, Hillebrand H, (2011) Empirical approaches to metacommunities: A review and comparison with theory. Trends in Ecology & Evolution, 26, 482–491. |
| [40] | Magurran AE, Mcgill BJ (2010) Biological Diversity:Frontiers in Measurement and Assessment. OUP Oxford. Oxford University Press, Oxford. |
| [41] | McArdle BH, Anderson MJ (2001) Fitting multivariate models to community data: A comment on distance-based redundancy analysis. Ecology, 82, 290-297. |
| [42] | McLaughlin P, Krause K, Maloney K, Woods T, Wagner T (2024) Evaluating the effectiveness of joint species distribution modeling for freshwater fish communities within large watersheds. Canadian Journal of Fisheries and Aquatic Sciences, 81, 1248-1263. |
| [43] | Niku J, Hui FKC, Taskinen S, Warton DI (2019) Gllvm: Fast analysis of multivariate abundance data with generalized linear latent variable models in R. Methods in Ecology and Evolution, 10, 2173-2182. |
| [44] | Norberg A, Abrego N, Blanchet FG, Adler FR, Anderson BJ, Anttila J, Araújo MB, Dallas T, Dunson D, Elith J, Foster SD, Fox R, Franklin J, Godsoe W, Guisan A, O’Hara B, Hill NA, Holt RD, Hui FKC, Husby M, Kålås JA, Lehikoinen A, Luoto M, Mod HK, Newell G, Renner I, Roslin T, Soininen J, Thuiller W, Vanhatalo J, Warton D, White M, Zimmermann NE, Gravel D, Ovaskainen O (2019) A comprehensive evaluation of predictive performance of 33 species distribution models at species and community levels. Ecological Monographs, 89, e01370. |
| [45] | Odriozola I, Abrego N, Tláskal V, Zrůstová P, Morais D, Větrovský T, Ovaskainen O, Baldrian P (2021) Fungal communities are important determinants of bacterial community composition in deadwood. mSystems, 6, e01017-e01020. |
| [46] | Oksanen J, Blanchet FG, Kindt R, Legendre P, Minchin PR, O Hara RB, Simpson GL, Solymos P, Stevens MHH, Wagner H (2013) Package ‘vegan’. Community Ecology Package, Version 2, 1-295. https://cran.r-project.org/. (accessed on 2026-01-10) |
| [47] | Ovaskainen O, Abrego N (2020) Joint Species Distribution Modelling. Cambridge University Press, Cambridge. |
| [48] | Ovaskainen O, Hottola J, Siitonen J (2010) Modeling species co-occurrence by multivariate logistic regression generates new hypotheses on fungal interactions. Ecology, 91, 2514-2521. |
| [49] | Ovaskainen O, Rybicki J, Abrego N (2019) What can observational data reveal about metacommunity processes? Ecography, 42, 1877-1886. |
| [50] | Ovaskainen O, Soininen J (2011) Making more out of sparse data: Hierarchical modeling of species communities. Ecology, 92, 289-295. |
| [51] | Ovaskainen O, Tikhonov G, Norberg A, Guillaume Blanchet F, Duan L, Dunson D, Roslin T, Abrego N (2017) How to make more out of community data? A conceptual framework and its implementation as models and software. Ecology Letters, 20, 561-576. |
| [52] | Ovaskainen O, Winter S, Tikhonov G, Abrego N, Anslan S, de Waard JR, de Waard SL, Fisher BL, Furneaux B, Hardwick B, Kerdraon D, Pentinsaari M, Raharinjanahary D, Rajoelison ET, Ratnasingham S, Somervuo P, Sones JE, Zakharov EV, Hebert PDN, Roslin T, Dunson D (2025) Common to rare transfer learning (CORAL) enables inference and prediction for a quarter million rare Malagasy arthropods. Nature Methods, 22, 2074-2082. |
| [53] | Pichler M, Hartig F (2021) A new joint species distribution model for faster and more accurate inference of species associations from big community data. Methods in Ecology and Evolution, 12, 2159-2173. |
| [54] | Poggiato G, Münkemüller T, Bystrova D, Arbel J, Clark JS, Thuiller W (2021) On the interpretations of joint modeling in community ecology. Trends in Ecology & Evolution, 36, 391-401. |
| [55] | Pollock LJ, Tingley R, Morris WK, Golding N, O’Hara RB, Parris KM, Vesk PA, McCarthy MA (2014) Understanding co-occurrence by modelling species simultaneously with a Joint Species Distribution Model (JSDM). Methods in Ecology and Evolution, 5, 397-406. |
| [56] | Powell-Romero F, Fountain-Jones NM, Norberg A, Clark NJ (2023) Improving the predictability and interpretability of co-occurrence modelling through feature-based joint species distribution ensembles. Methods in Ecology and Evolution, 14, 146-161. |
| [57] | Rahman AU, Tikhonov G, Oksanen J, Rossi T, Ovaskainen O (2024) Accelerating joint species distribution modelling with Hmsc-HPC by GPU porting. PLoS Computational Biology, 20, e1011914. |
| [58] | Runquist RDB, Lake TA, Moeller DA (2021) Improving predictions of range expansion for invasive species using joint species distribution models and surrogate co-occurring species. Journal of Biogeography, 48, 1693-1705. |
| [59] | Sallinen S, Norberg A, Susi H, Laine AL (2020) Intraspecific host variation plays a key role in virus community assembly. Nature Communications, 11, 5610. |
| [60] | Schliep EM, Lany NK, Zarnetske PL, Schaeffer RN, Orians CM, Orwig DA, Preisser EL (2018) Joint species distribution modelling for spatio-temporal occurrence and ordinal abundance data. Global Ecology and Biogeography, 27, 142-155. |
| [61] | Schmitt S, Pouteau R, Justeau D, de Boissieu F, Birnbaum P (2017) ssdm: An R package to predict distribution of species richness and composition based on stacked species distribution models. Methods in Ecology and Evolution, 8, 1795-1803. |
| [62] | Smith JA, Johnson DD (2024) Evaluating drivers and predictability of catch composition in a highly mixed trawl fishery using stacked and joint species distribution models. Fisheries Research, 279, 107151. |
| [63] | Stephenson F, Bowden DA, Rowden AA, Anderson OF, Clark MR, Bennion M, Finucci B, Pinkerton MH, Goode S, Chin C, Davey N, Hart A, Stewart R (2024) Using joint species distribution modelling to predict distributions of seafloor taxa and identify vulnerable marine ecosystems in New Zealand waters. Biodiversity and Conservation, 33, 3103-3127. |
| [64] | Thorson JT, Ianelli JN, Larsen EA, Ries L, Scheuerell MD, Szuwalski C, Zipkin EF (2016) Joint dynamic species distribution models: A tool for community ordination and spatio-temporal monitoring. Global Ecology and Biogeography, 25, 1144-1158. |
| [65] | Tikhonov G, Duan L, Abrego N, Newell G, White M, Dunson D, Ovaskainen O (2020) Computationally efficient joint species distribution modeling of big spatial data. Ecology, 101, e02929. |
| [66] | Tikhonov G, Opedal ØH, Abrego N, Lehikoinen A, de Jonge MMJ, Oksanen J, Ovaskainen O (2020) Joint species distribution modelling with the R-package HMSC. Methods in Ecology and Evolution, 11, 442-447. |
| [67] | Traylor CR, Ulyshen MD, McHugh JV, Burner RC (2024) Forest age is a primary trait filter for saproxylic beetles in the southeastern United States. Forest Ecology and Management, 553, 121545. |
| [68] | Vellend M (2010) Conceptual synthesis in community ecology. The Quarterly Review of Biology, 85, 183-206. |
| [69] | Violet C, Boyé A, Chevalier M, Gauthier O, Grall J, Marzloff MP (2022) A multifaceted framework to assess tradeoffs in interpretability, Explanatory and Predictive Performances of Alternative Joint Species Distribution Models. bioRxiv, https://doi.org/10.1101/2022.12.19.519605. (accessed on 2026-01-10) |
| [70] | Wang HY, Chen XL, Chen SC (2025) Chinese Seed Trait Database: A curated resource for diaspore traits in the Chinese flora. New Phytologist, 248, 11-16. |
| [71] | Warton DI, Blanchet FG, O’Hara RB, Ovaskainen O, Taskinen S, Walker SC, Hui FKC (2015) So many variables: Joint modeling in community ecology. Trends in Ecology & Evolution, 30, 766-779. |
| [72] | Weigel B, Graco-Roza C, Hultman J, Pajunen V, Teittinen A, Kuzmina M, Zakharov EV, Soininen J, Ovaskainen O (2023) Local eukaryotic and bacterial stream community assembly is shaped by regional land use effects. ISME Communications, 3, 65. |
| [73] | Weiss S, Van Treuren W, Lozupone C, Faust K, Friedman J, Deng Y, Xia LC, Xu ZZ, Ursell L, Alm EJ, Birmingham A, Cram JA, Fuhrman JA, Raes J, Sun FZ, Zhou JZ, Knight R (2016) Correlation detection strategies in microbial data sets vary widely in sensitivity and precision. The ISME Journal, 10, 1669-1681. |
| [74] | Wilkinson DP, Golding N, Guillera-Arroita G, Tingley R, McCarthy MA (2019) A comparison of joint species distribution models for presence-absence data. Methods in Ecology and Evolution, 10, 198-211. |
| [75] | Wilkinson DP, Golding N, Guillera-Arroita G, Tingley R, McCarthy MA (2021) Defining and evaluating predictions of joint species distribution models. Methods in Ecology and Evolution, 12, 394-404. |
| [76] | Wisz MS, Pottier J, Kissling WD, Pellissier L, Lenoir J, Damgaard CF, Dormann CF, Forchhammer MC, Grytnes JA, Guisan A, Heikkinen RK, Høye TT, Kühn I, Luoto M, Maiorano L, Nilsson MC, Normand S, Öckinger E, Schmidt NM, Termansen M, Timmermann A, Wardle DA, Aastrup P, Svenning JC (2013) The role of biotic interactions in shaping distributions and realised assemblages of species: Implications for species distribution modelling. Biological Reviews, 88, 15-30. |
| [77] | Zobel M (1997) The relative of species pools in determining plant species richness: An alternative explanation of species coexistence? Trends in Ecology & Evolution, 12, 266-269. |
| [78] | Zhang JT (2011) Quantitative Ecology, 2nd edn. Science Press, Beijing. (in Chinese) |
| [张金屯 (2011) 数量生态学(第二版). 科学出版社, 北京.] | |
| [79] | Zhu YJ, Shan D, Zhang X, Liu YS, Shi ZJ, Yang XH (2018) Advances in joint species distribution models to reveal community structure and its environmental response. Chinese Journal of Applied Ecology, 29, 4217-4225. (in Chinese with English abstract) |
| [朱媛君, 山丹, 张晓, 刘艳书, 时忠杰, 杨晓晖 (2018) 揭示群落结构及其环境响应的联合物种分布模型的研究进展. 应用生态学报, 29, 4217-4225.] |
| [1] | 邹怡. α多样性指数选择: 不等量采样下的模拟比较[J]. 生物多样性, 2026, 34(1): 25278-. |
| [2] | 陈长樵, 冯艳飞, 卢力奇, 何怀江, 张春雨, 赵秀海, 郝珉辉. 吉林蛟河针阔混交林β多样性格局及其形成机制[J]. 生物多样性, 2025, 33(12): 25169-. |
| [3] | 施国杉, 刘峰, 曹光宏, 陈典, 夏尚文, 邓云, 王彬, 杨效东, 林露湘. 西双版纳热带季节雨林木本植物的beta多样性: 空间、环境与林分结构的作用[J]. 生物多样性, 2024, 32(12): 24285-. |
| [4] | 王彦平, 张敏楚, 詹成修. 嵌套分布格局研究进展: 分析方法、影响机制及保护应用[J]. 生物多样性, 2023, 31(12): 23314-. |
| [5] | 王健铭, 雷训, 冯益明, 吴波, 卢琦, 何念鹏, 李景文. 中国温带荒漠植物群落生态特异性格局及其影响因素[J]. 生物多样性, 2023, 31(10): 23144-. |
| [6] | 董建宇, 孙昕, 詹启鹏, 张宇洋, 张秀梅. 莱州湾东岸潮下带大型底栖动物群落beta多样性格局及其驱动因素[J]. 生物多样性, 2022, 30(3): 21388-. |
| [7] | 曲梦君, 努尔依拉·阿巴拜克, 邹旭阁, 赵航, 朱威霖, 王健铭, 李景文. 地理距离和环境因子对阿拉善戈壁植物群落β多样性的影响[J]. 生物多样性, 2022, 30(11): 22029-. |
| [8] | 张健, 孔宏智, 黄晓磊, 傅声雷, 郭良栋, 郭庆华, 雷富民, 吕植, 周玉荣, 马克平. 中国生物多样性研究的30个核心问题[J]. 生物多样性, 2022, 30(10): 22609-. |
| [9] | 邹怡. 样本量不一致时的β多样性计算[J]. 生物多样性, 2021, 29(6): 790-797. |
| [10] | 姚志良,温韩东,邓云,曹敏,林露湘. 哀牢山亚热带中山湿性常绿阔叶林树种beta多样性格局形成的驱动力[J]. 生物多样性, 2020, 28(4): 445-454. |
| [11] | 高梅香, 林琳, 常亮, 孙新, 刘冬, 吴东辉. 土壤动物群落空间格局和构建机制研究进展[J]. 生物多样性, 2018, 26(10): 1034-1050. |
| [12] | 王健铭, 王文娟, 李景文, 冯益明, 吴波, 卢琦. 中国西北荒漠区植物物种丰富度分布格局及其环境解释[J]. 生物多样性, 2017, 25(11): 1192-1201. |
| [13] | 张姗, 蔺菲, 原作强, 匡旭, 贾仕宏, 王芸芸, 索炎炎, 房帅, 王绪高, 叶吉, 郝占庆. 长白山阔叶红松林草本层物种多度分布格局及其季节动态[J]. 生物多样性, 2015, 23(5): 641-648. |
| [14] | 裴男才, 张金龙, 米湘成, 葛学军. 植物DNA条形码促进系统发育群落生态学发展[J]. 生物多样性, 2011, 19(3): 284-294. |
| [15] | 牛红玉, 王峥峰, 练琚愉, 叶万辉, 沈浩. 群落构建研究的新进展: 进化和生态 相结合的群落谱系结构研究[J]. 生物多样性, 2011, 19(3): 275-283. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||
备案号:京ICP备16067583号-7
Copyright © 2026 版权所有 《生物多样性》编辑部
地址: 北京香山南辛村20号, 邮编:100093
电话: 010-62836137, 62836665 E-mail: biodiversity@ibcas.ac.cn
![]()