

|
|
||
|
基于3种线粒体标记探讨中日沿海角木叶鲽遗传多样性差异
生物多样性
2022, 30 (5):
21485-.
DOI: 10.17520/biods.2021485
角木叶鲽(Pleuronichthys cornutus)是东亚沿海重要的鲽形目经济鱼类, 为更好地保护和开发利用其种质资源, 有必要全面了解其遗传背景。本研究测定了中国和日本沿海7个群体200尾角木叶鲽线粒体控制区(CR) 5'端、细胞色素b (Cytb)和NADH脱氢酶第二亚基(ND2)基因序列, 比较不同标记在解析遗传多样性和种群结构上的可行性与有效性, 阐明中日沿海角木叶鲽群体间出现遗传分化的分子机制。CR序列分析发现中日沿海7个角木叶鲽群体遗传多样性表现出较高的单倍型多样性(Hd = 0.9699)和较低的核苷酸多样性(π = 0.0061); 各群体间无显著的遗传分化(FST = -0.0197-0.0184, P > 0.05); 单倍型网络未显示出明显的地理聚群和谱系结构; 分子方差分析(AMOVA)表明变异主要发生在群体内部(> 99.17%)。进一步通过Cytb和ND2基因分别与CR序列对比分析, 结果表明群体遗传多样性均表现为高Hd (0.9683-0.9829)低π (0.0050-0.0063)模式, 仅有ND2基因分析FST值(FST = 0.0302, P < 0.05)显示了中国碣石(GDJS)和日本明石(JAP)群体间显著的低水平遗传分化现象。CR、Cytb和ND2的单倍型网络图均无明显的地理聚类和谱系结构, AMOVA分析也显示变异主要来源于群体内(> 98.39%)。种群历史动态分析结果显示, 角木叶鲽可能在第四纪中更新世晚期经历了群体扩张事件, 扩张时间分别为31.93-9.58万年前(CR)、27.53-22.02万年前(Cytb)和26.99-18.75万年前(ND2)。综上所述, 中日沿海的角木叶鲽具有较高遗传多样性, GDJS和JAP群体间存在低度分化; ND2基因比CR和Cytb序列更适于分析角木叶鲽种群遗传结构, 选择多个遗传标记可有效弥补单一标记分析遗传多样性的局限性; 推测冰期两大独立避难所的形成及GDJS和JAP群体距离相隔较远是其发生遗传分化的主要原因。研究结果为中日沿海角木叶鲽渔业资源的种质保护与可持续利用提供了理论依据。 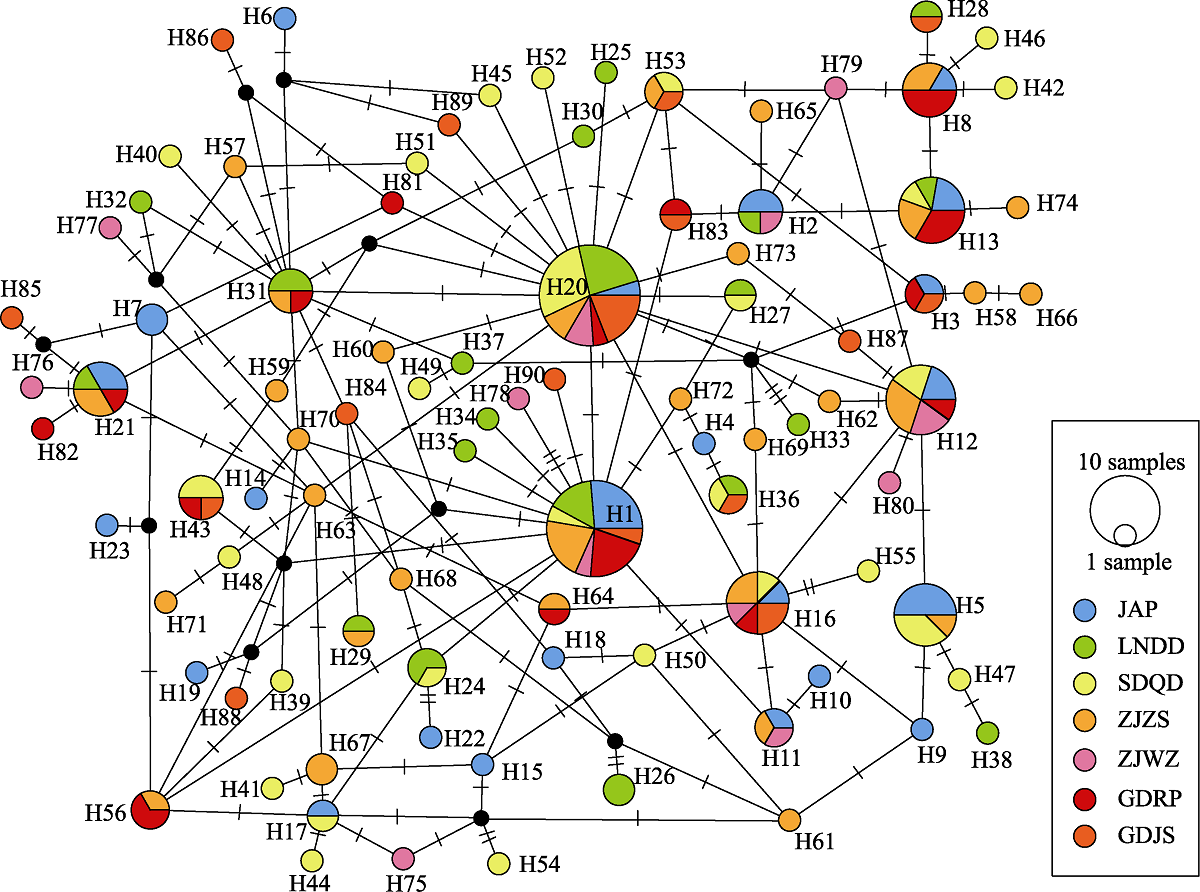 View image in article
图1
7个角木叶鲽群体的CR序列单倍型网络图。不同的填充颜色代表不同的种群; 节点大小与单倍型频率相对应; “1 sample”的节点大小为1个个体, “10 samples”则为10个个体; 黑点表示理论上存在但未被监测到的单倍型; 圆圈之间的短横线代表突变。地点代号同
正文中引用本图/表的段落
角木叶鲽CR序列的变异位点数对应着90个单倍型(编号H1-H90), 其中H1和H20为7个群体所共享, 其余大部分单倍型为独享单倍型。基于K2-P模型的CR单倍型网络图(图1)显示位于网络中心的H20为主体单倍型, 来自日本群体(JAP)的单倍型散乱无序分布于各个分支, 不同来源的群体单倍型没有形成明显的地理结构和谱系结构。各单倍型突变步数在1-3步之间, 说明各单倍型间差异较小。
基于角木叶鲽的CR、Cytb和ND2基因在K2-P模型下分别建立单倍型网络(图2)。由CR的74个单倍型(编号H1-H74)构建的单倍型网络显示与图1相似, 无明显的地理聚群和谱系结构。
本文的其它图/表
|